���w������M�W�ļ{������ˮ�н�ʾ�S���ķǽ��亣��
��Nature Microbiology����Single-particle genomics uncovers abundant non-canonical marine viruses from nanolitre volumes
�����w��
��
��
С
��
�r�g��2025��11��06��
��Դ��Nature Microbiology 19.4
�����]��
�������о�ᘌ����������Բ��@��������ƿ�i���_�l�˭h���^�һ���M�W(EMCG)���g��ͨ�^��300�{����ˮ�ӱ���2,037���w���M�І��w������M�y�ɹ��l�F�˴���δ�����y�����M�W�z�y����Naomiviridae����ǽ���DNA�������@Щ����ʹ��Ó������(dU)���Ó������(dT)����ʾ�˺���Ȧ�д�ǰ����ҕ����Ҫ���B�Ⱥ��
����
�������^�����������M�����أ����в����������S��������w֮һ���ں������Bϵ�y�а������P�I��ɫ��Ȼ�������y���о������ڽ�ʾ���������������Է������R�������𡣺����M�W�mȻ�܉��ṩ����Ⱥ������wҕ�D�������ڲ����ĸ߶������Ժ��l���Ļ���M���D�ƣ��@�õIJ��������M�M�b����M(vMAGs)����Ƭ�λ��Ҳ������������ڟɹ⼤������x(FAVS)�Ćβ�������M�W�mȻ�܉�@�ø������IJ�������M����ͨ�����������ڹ�W�z�y�`���ȣ��y�Բ��@С�Ͳ����w����
���@헰l���ڡ�Nature Microbiology�����о��У��о��ˆT�_�l��һ�N����h���^�һ���M�W(EMCG)�ĸ����Լ��g���麣���о��_������;����ԓ���gͨ�^����Ʒ�е��w���S�C�ָ���Ƥ�����İ����z��(SPC)�У���ÿ���z�҃��M��DNA�U���͗l�δa��ӛ�����F�ˏĘOС��Ʒ�w�e���H300�{����ˮ���и�Ч�@ȡ��ǧ�����w������M���С�
�P�I���g����������ʹ�ð����z��(SPC)����ˮ�ӱ��M���^�һ�̎�������z�҃��M�ЉA���ѽ��ȫ����M�U��(WGA-X)���M�ϗl�δa��ӛ���g���F���w��ۙ��Illumina�y���������Ϣ�W�������ӱ�����2022��4��18����������˼ؐ�۲ɼ��ĺ�ˮ��
�w�����@�Ķ����c�b��
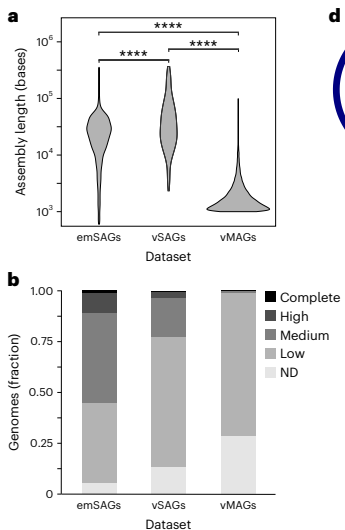
�о��ˆT�_�l��ԇ����EMCG������ԓ�������ڌ�ˮ�ӷָ���SPCs�ȡ�ͨ�^����300�{����������ˮ�ӱ����@����2,037���ΔU������M������SPCռ���ʺ͜y��emSAGs�ķ��עጣ���Ӌԭ�˸������:����DNA�������w�����S�ȷքe��1.93��109 L-1��1.79��1010 L-1���c��ʽ����Ӌ���Y���߶�һ�£�����emSAGs�܉����S�Cȡ�ӡ����w�Եķ�ʽ�������������ӱ��е�DNA�w����
��emSAGs�M�г�������@ʾ��������emSAGsռ������λ��1,791������������emSAGs��193����������9:1���c������没���c������ƽ�����������������emSAGs�ķ�M���cͬһ�ӱ���ԭ�˸�������cSAGs���ƣ����cͬһ����λ�õļ����о�һ�¡�
�����ӻ���M�M�b���|��
�����ӻ���M���е��|�������N�����g���ڲ��������emSAGs��ƽ���L�ȣ�27 kbp����vMAGs��2 kbp����10�����ϣ�������vSAGs��56 kbp����CheckV�u���@ʾemSAGs�и��|�����е��|������M�M�b�ı�����54%�����ں����M�دBȺ��1%����vSAGs��22%��������EMCG�ڻ��ո��|������M���惞�ں����M�W��FAVS��
ͨ�^�W�j������emSAGs��vMAGs��鲡���������Ԫ(vOTUs)���Y���@ʾ�����emSAGs��vMAGs���c��������M�M�b�������ɆT��Ⱥ���Ҋ�������Ƕ���vMAGs�c��emSAG�����ӳ��emSAGs�M�b�������h����vMAGs��
�ǽ���DNA�w���������S��
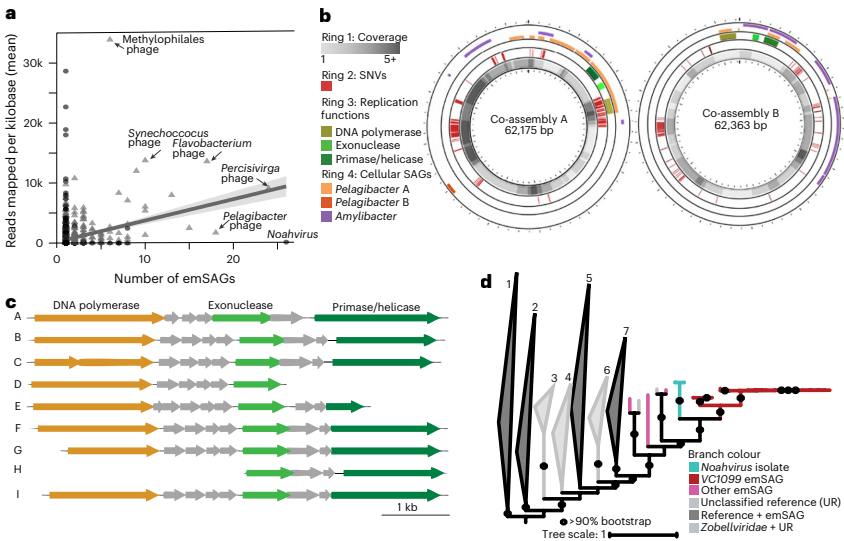
�о�����l�F������emSAGs�Ĵ��Ͳ����ӻ���M��Ⱥ(vOTUs)�c���������M�x���������P���^������emSAGs��������vOTU��26�����]����ļ���κβ��������M�x����Ҳ�]��vMAG�ɆT���@��������emSAGs��vMAGs�M�ɵIJ���H�ɺ����M�M�bƬ�λ�����߀�c�@ȡ��DNA��Դ��ͬ���P��
�Mһ�������@ʾ���@Щȱ�������M�����Ե��S��vOTU����VC1099��Ⱥ������Naomiviridae�Ƶ�Noahvirus�����B������1.8%�IJ�����emSAGs���ஔ�ژӱ����S�ȼs3��108 L--1�����VC1099������EMCG�l�F��һ���cNoahvirus���P���S�������Vϵ�������y���������M�W�o���z�y���@Щ������
Noahvirus���ص�ʹ�÷ǽ��������dU���dT�������Mֻ����phi29�ۺ�ø�����®a������DNA��ؐ����ܜy��EMCG���������漰ʹ��phi29�ۺ�ø�U�����w����gDNA���@�����Naomiviridae��emSAGs�еĻ��ա������������M�y��]���M���A�U��������A�U�����ڻ��Ⱥ���B�����y�����������ƫ�
��VC1099 emSAGs����contigs�M�й��M�b�a���˃ɂ��h�����M�b���L�ȼs62 kbp���c�Ѱl����Noahvirus���x�����M�L�����ơ��Ȍ�������ʾ�ˆ�Naomiviridae�w���g���l�ʵĺ�����ˮƽ׃����ͨ�^�����c�ɂ�VC1099���M�b���Ƶ�contigs���ڼ���SAGs�аl�F�cNaomiviridae���P��СƬ�Ό��R����������ܸ�Ⱦ���������S���ĸ��μ����Vϵ������Rhodobacteraceae�Ƶ�Amylibacter��Pelagibacteraceae�Ƶ�Pelagibacter��
�о��YՓ�c���x
�h���^�һ���M�W(EMCG)����һ�N���ͷ�������h����Ʒ�І������ͼ������z��Ԫ�صĸ�ͨ������������M�y���ṩ����ƽ�_��ԓ����ͨ�^����Ʒ�е��w���M���S�C�^�һ����o����s���F�x�����Ɍ��F��ǧ���w���Ĝy���@������˷���ͨ�����������O��ɱ���
�о�����Ҫ�İl�F֮һ�ǽ�ʾ�˺�ˮ��Naomiviridae���S���ȣ�������������Ⱦ�N���S���ĺ����μ����Vϵ���@Щ����ʹ��dU����dT�ķǽ���DNA��������������ӱ���������ϵ�y�ęz�y���о��Y�����������зǽ���DNA�IJ������ض�����^����ܷdz��S�������ں����������B�W�а����P�I��ɫ��Ȼ���˜ʺ����M�W�����o���z�y���@Щ������
EMCG���g�麣��������h���в����������������z��Ԫ�صĶ�������M���ݷ����ṩ���C��������ˮ��Naomiviridae�ձ��Եİl�F��ӳ������҂������зǽ���DNA�ļ������z��Ԫ�ص��S�ȡ����B���ú����\�g�����������Ҫ�ԡ�EMCG�ā�����Ʒ�w�e���Ԇ��w���ֱ��ʽ����������������M���ݵ�������Ҳ�����ڭh������W֮����I���ҵ����ã����Ⱦ�\��ͷ��t�W��
 ����ͨ�Ź���̖
����ͨ�Ź���̖
 ����ͨ������
����ͨ������
- ����
- ���H
- ����
- ����
- �a�I
- ���c
- ����
���ՄӑB |
�˲��Ј� |
�¼��g���� |
�Ї��ƌW�� |
��չ�_ |
BioHot |
���v��ֱ�� |
��չ���� |
�r���� |
���g��Ӎ |
���Mԇ��
������� ����ͨ
Copyright© eBiotrade.com, All Rights Reserved
ϵ���䣺
��ICP��09063491̖




 ����ͨ�Ź���̖
����ͨ�Ź���̖